Retour d’expérience après des essais de combinaison des technologies de multiplexages Xenium et Hyperion sur une seule lame – Julien Faget (IRCM – Montpellier)
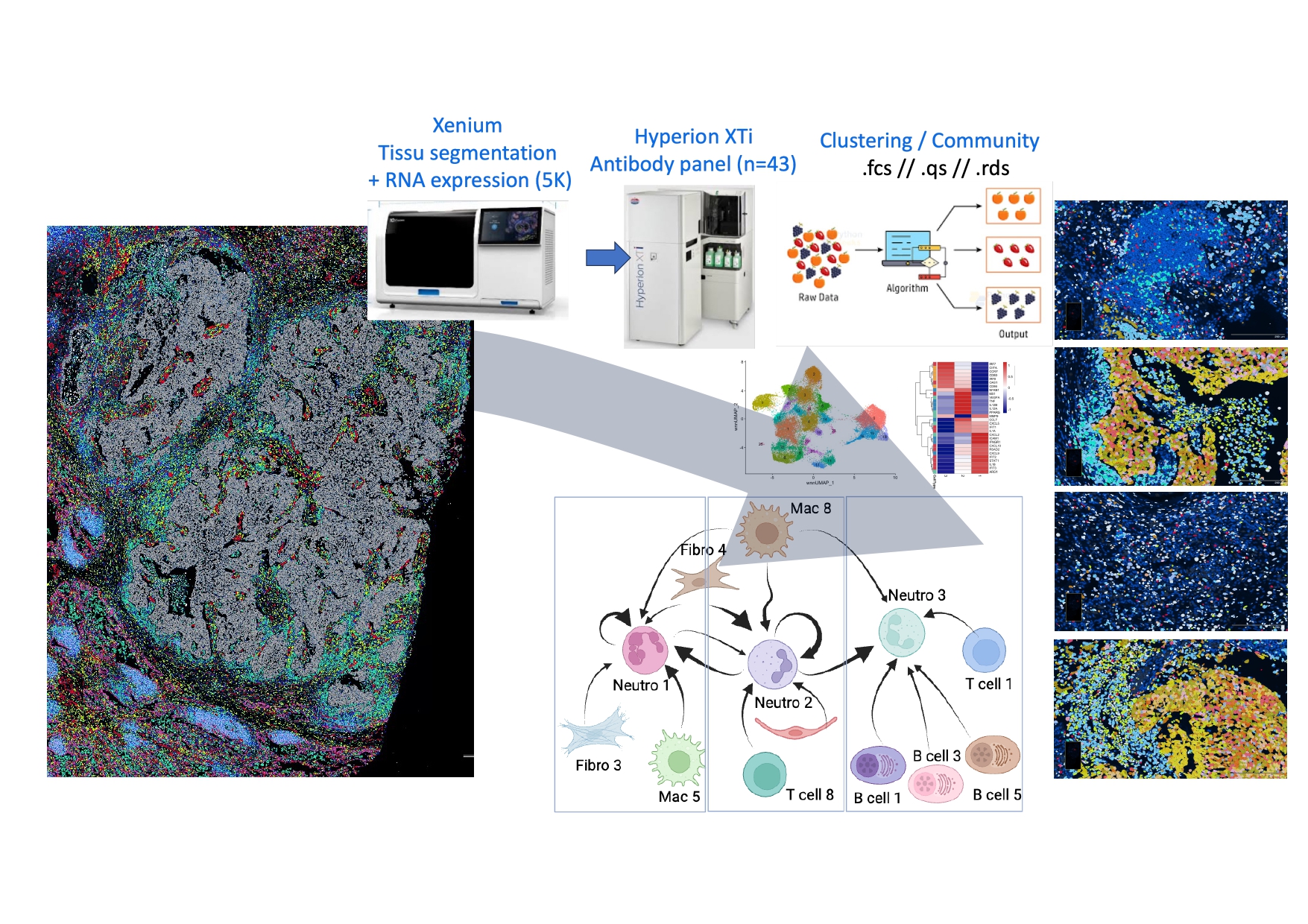
La biologie spatiale regroupe aujourd’hui un ensemble de technologies permettant de mettre en lumière les relations cellules/cellules qui gouvernent l’architecture des tissus complexes. Il ne s’agit pas d’envoyer des souris en orbite, mais de disséquer l’organisation des tissus en mesurant le plus grand nombre de paramètres possible avec la plus haute résolution possible, tout en conservant leurs coordonnées de localisation sur une coupe histologique. La biologie spatiale multiomique consiste à combiner plusieurs technologies, si possible sur la même coupe, afin de mesurer des paramètres de natures différentes, comme l’expression des gènes au niveau de l’ARN messager et l’expression de protéines par l’utilisation d’anticorps spécifiques. Durant mon intervention, je vous présenterai les résultats que nous avons obtenus en combinant la technologie Xenium de transcriptomique spatiale et la technologie Hyperion de protéomique spatiale sur une coupe de cancer du poumon humain. Grâce au développement méthodologique réalisé par la plateforme SIM-CaT de l’Institut de recherche en cancérologie de Montpellier, nous avons pu analyser l’expression de 5 000 gènes et 43 protéines avec une résolution subcellulaire. L’application d’un masque de segmentation commun aux deux images a permis d’obtenir un jeu de données à l’échelle de la cellule unique, tout en préservant la localisation et la forme des cellules sur la coupe histologique. Ceci offre l’opportunité d’observer les communautés cellulaires constituant le microenvironnement tumoral. Il a alors été possible d’annoter et de localiser 75 sous-populations de cellules par une analyse multimodale, et d’obtenir l’expression de programmes génétiques et de marqueurs protéiques liés à leur localisation et à leur fonction.
Intervenant
-
 Julien Faget
Julien Faget